Klienti naší sekvenační laboratoře často požadují přípravu sekvenačních knihoven pomocí rRNA deplece (ribodeplece), tedy včetně odstranění rRNA. Jelikož se někdy setkáváme s tím, že výsledky odstranění rRNA jsou neuspokojivé, prováděli jsme v naší laboratoři níže popsané testy. Jejich cílem bylo poskytnout bližší vysvětlení toho, v čem je v případě rRNA-depletovaných knihoven „zakopaný pes“, a současně poskytnout nějaká doporučení vám, našim zákazníkům, jak připravovat celkovou RNA pro tento typ analýz.
Úvodem
Ribozomální RNA (rRNA) je nejvíce zastoupenou složkou (> 80 %) v celkové (total) RNA izolované z buněk či tkání. Pro řadu aplikací je však rRNA nepodstatná. Jejím sekvenováním se zbytečně navyšuje potřebná sekvenační kapacita a v konečném důsledku i cena laboratorní a datové analýzy.
V prvním kroku přípravy RNA-seq knihoven je tedy více než žádoucí se této nepotřebné rRNA zbavit. V současné době je k dispozici několik protokolů, které pro tyto účely používají různé strategie. Tyto metody mají přirozeně své silné a slabé stránky.
Nejběžnější forma přípravy sekvenační knihovny začíná nabohacováním zralých poly-A transkriptů hybridizací na oligo- (dT) magnetické kuličky. Pro přípravu RNA-seq knihovny jsou následně použity pouze tyto specificky navázané fragmenty. Řečeno polopaticky, z celkové RNA „vytáhneme“ pro potřebu dalšího zpracování pouze ty molekuly, které mají poly-A konec. Výhodou tohoto přístupu je, že sekvenační knihovny jsou vytvořeny na základě transkriptů kódujících proteiny, což je ideální například pro srovnávací analýzu genové exprese. Tato metoda tzv. poly-A selekce se používá pro většinu transkriptomových studií také proto, že jí požadovaná hloubka sekvenování je relativně nízká.
V některých situacích však tato metoda selhává. Jednou z nich je druhová kompatibilita – poly-A selekci lze použít pouze u eukaryotních organismů, u kterých k polyadenylaci dochází. Není tedy použitelná např. u bakterií. Důležitá je také skutečnost, že v případě poly-A RNA-seq knihoven je kvalita dat výrazně ovlivněna integritou celkové RNA. Pakliže vstupní materiál vykazuje vyšší míru degradace, následkem může být významné zkreslení dat směrem k 3' oblasti. A samozřejmě v neposlední řadě je potřeba si uvědomit, že použitím této metody jsme schopni sekvenovat pouze a jenom RNA nesoucí poly-A konec, nezískáme tak informace o nezralé pre-mRNA, nekódujících transkriptech a všech dalších RNA molekulách nemajících poly-A konec.
Druhou metodou pro odstranění rRNA je použití speciálně navržených záchytných sond, které specificky hybridizují s rRNA (my používáme DNA sondy). Takto navázaná rRNA je následně magneticky či enzymaticky odstraněna a zbylý materiál je použit pro přípravu RNA-seq knihovny. Řečeno opět polopaticky, pro potřebu dalšího zpracování z celkové RNA „vyhodíme“ rRNA molekuly. Mluvíme o tzv. ribodepleci.
Přestože při výběru této metody je nutné počítat s tím, že v některých případech je zapotřebí až dvakrát vyšší sekvenační kapacita, aby bylo dosaženo stejné úrovně citlivosti detekce pro analýzu genové exprese, přináší tato metoda některé významné výhody. Deplece rRNA nabízí atraktivní možnost pro současnou detekci kódujících i nekódujících RNA: mRNA, pre-mRNA a řadu dalších funkčně relevantních krátkých i dlouhých nekódujících transkriptů. Poskytuje tedy výrazně více informací než prostá poly-A selekce. Další výhodou může být to, že metody rRNA deplece mohou být za určitých okolností použity pro sekvenování vzorků RNA s nižší integritou (ale samozřejmě i zde platí, že jakkoliv degradovaná RNA může negativně ovlivnit výstup a spolehlivost analýzy). Pro případnou analýzu takto problematických vzorků bychom proto z naší zkušenosti spíše doporučili protokol QuantSeq.
Obecně lze říci, že v případě dobře provedené ribodeplece bude rRNA představovat 5-10 % výsledných dat. Úspešnost ribodeplece, tedy odstranění rRNA, ale záleží na řadě faktorů.
Jak na úspěšnou ribodepleci
Prvním důležitým předpokladem úspěšné ribodeplece je použití správné soupravy kompatibilní s cílovým organismem. V tomto ohledu lze použít již předem navržené komerční sondy (např. Human/Mouse/Rat, Bacteria) nebo je možné si navrhnout vlastní sadu sond pro konkrétní organismus (zde je ovšem nutné počítat s vyššími náklady i větší časovou náročností). V této souvislosti stojí za upozornění fakt, že v případě rostlin není v současné době k dispozici spolehlivá a univerzální sada sond a je vždy žádoucí sondy pro konkrétní druh rostlin a typ rostlinného pletiva otestovat, případně optimalizovat jejich design.
Dalším zásadním předpokladem úspěchu ribodeplece je dostatečná kvantita a samozřejmě kvalita vstupního vzorku RNA. Zatímco koncentraci a integritu celkové RNA lze celkem jednoduše ověřit, detekce jiných parametrů je obtížnější. Mluvíme zejména o různých inhibitorech, které mohou být přítomny ve vzorku RNA (zejména soli, detergenty, alkoholy, enzymy apod.), a které mohou hrát zásadní roli v úspěšnosti ribodeplece, přičemž je v podstatě nemožné s jistotou říci, zda jsou přítomny či nikoliv. Tyto látky mohou jednak bránit úspěšné hybridizaci ribodeplečních sond k rRNA, díky čemuž dojde k nedokonalému odstranění rRNA ze vzorků, a/nebo mohou inhibovat probíhající enzymatické reakce. Ukázkovým příkladem může být závislost úspěšnosti ribodeplece na koncentraci specifických solí, přičemž jejich neoptimální koncentrace nebo současná přítomnost jiných nežádoucích solí může potřebnou iontovou rovnováhu velmi ovlivnit.
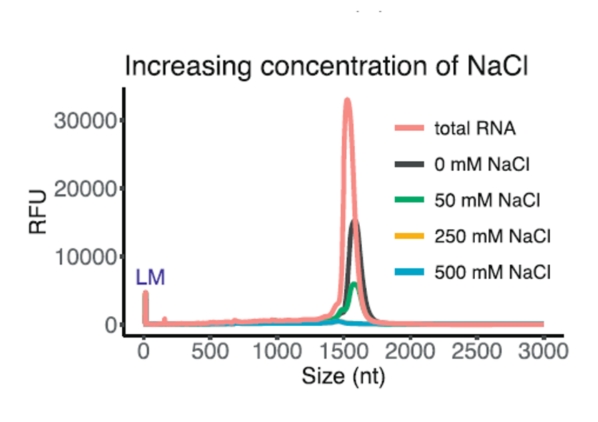
(převzato z Kim et al., Efficient depletion of ribosomal RNA for RNA sequencing in planarians, BMC Genomics (2019) 20:909)
V neposlední řadě může být problémem přítomnost gDNA ve vzorku, proto je žádoucí gDNA dokonale odstranit. Pokud je tato procedura provedena s pomocí enzymu DNáza I, je absolutně kritické enzym po reakci důkladně inaktivovat – v důsledku možné zbytkové aktivity DNázy I budou degradovat jednovláknové DNA sondy nezbytné pro depleci rRNA.
Problémem těchto analýz je, že jsou-li např. v RNA přítomny inhibitory hybridizace (a tedy ribodeplece), během přípravy knihovny to s jistotou nikdy nepoznáme. Provedeme ribodepleci, následně připravíme sekvenační knihovnu a teprve poté, kdy je tato sekvenována, můžeme s jistotou říci, zda byla ribodeplece úspěšná. Jenže v tu chvíli jsou již všechny peníze za analýzu utraceny a výsledkem je někdy zmar.
Vliv čistoty na kvalitu
V naší laboratoři jsme se proto zaměřili právě na tuto problematiku. Analyzovali jsme problematický testovací vzorek lidské celkové RNA a zaměřili jsme se na jeho kvalitu (čistotu) a následný vliv na účinnost ribodeplece. Ve všech případech byla použita stejná výchozí celková RNA, ale před samotnou ribodeplecí a vlastní přípravou sekvenační knihovny byla tato celková RNA opracována takto:
U takto připravených RNA-vzorků byla provedena deplece rRNA enzymatickou metodou. Její úspěšnost jsme předběžně ověřili pomocí citlivé kapilární elektroforézy. Z výsledku je patrné, že u vzorků A a B byla většina rRNA odstraněna, u vzorku C nikoliv.
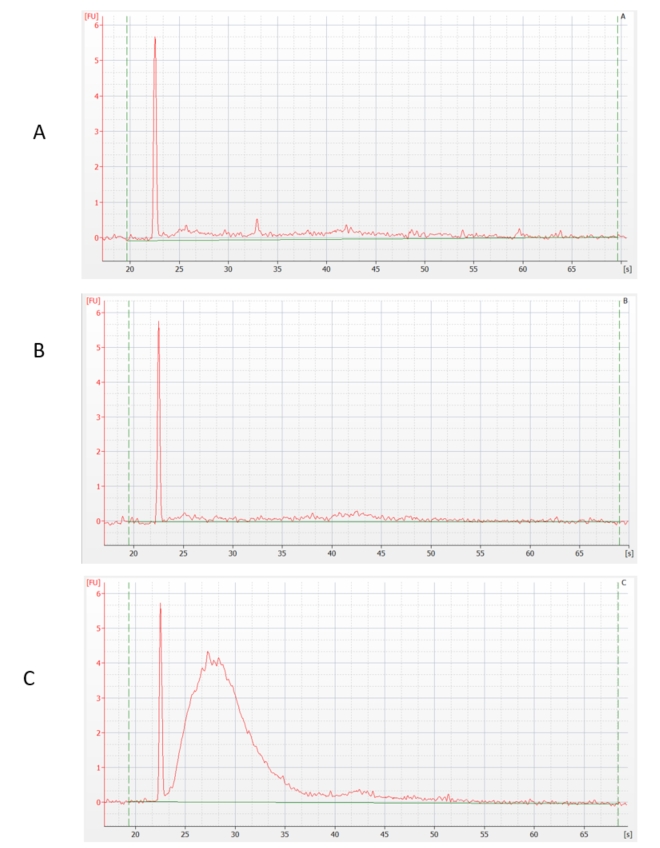
Dále byla změřena koncentrace RNA. Úbytek RNA po ribodepleci byl: vzorek A - 80 %, vzorek B - 90 %, vzorek C - 0 %, což předchozí tvrzení potvrdilo. (Tyto verifikační kroky se při přípravě rRNA-depletovaných knihoven standardně neprovádí, poněvadž množství materiálu, s kterým se pracuje, to neumožňuje – pro potřeby testu bylo použito nadstandardní množství celkové RNA.)
Následně byly připraveny sekvenační knihovny a sekvenovány rutinním postupem. Získaná hrubá data byla mapována pomocí programu bwa (alignment via Burrows-Wheeler transformation; v0.7.17-r1188) na základě algoritmu BWA-MEM v defaultním nastavení na SILVA rRNA databázi (release 126) a zároveň na lidskou cDNA referenční sekvenci (GRCh38) s následujícími výsledky:
| Vzorek | Počty readů mapujících na rDNA (SILVA) | % rRNA ve vzorku |
| A | 121379 (z celkových 2260692) | 5,3 |
| B | 119405 (z celkových 2150301) | 5,5 |
| C | 1725514 (z celkových 2153394) | 80,1 |
U vzorků A a B, které byly před zpracováním přečištěny, byl tedy obsah rRNA v datech pouze asi 5 %. Toto číslo lze považovat za úspěšně proběhlou ribodepleci. Ve vzorku C, u kterého byl předpoklad přítomnosti nespecifických inhibitorů, byl obsah rRNA v datech 80 %. Účinnost ribodeplece je tudíž u tohoto vzorku více než neuspokojivá.
Výsledná data se tedy shodují s naším předpokladem, že ve vzorku C přítomnost blíže neurčených inhibitorů negativně ovlivnila úspěšnost ribodeplece a v zásadě znehodnotila experiment.
Souhrn
Dovolujeme si závěrem konstatovat, že čistota RNA, dodávané pro tento typ analýz do naší laboratoře, je plně pod vaší kontrolou! Velmi proto doporučujeme, abyste před zasláním vzorků do naší laboratoře vzorky skutečně dobře přečistili, nejlépe pomocí AMPure XP beads. Vyhnete se tak nemilému překvapení v podobě velmi vysokého zastoupení rRNA v datech poté, co vám dodáme výsledky. Musíte ale počítat s tím, že ztráty vstupního materiálu během přečištění mohou být dle našich zkušeností až 40 %.
NGS Lab, ngs@seqme.eu